中国科学院微生物研究所、中国微生物学会主办
文章信息
- 吕原野, 张益豪, 王博祥, 李承, 张浩千, 欧阳颀
- Lü Yuanye, Zhang Yihao, Wang Boxiang, Li Cheng, Zhang Haoqian, Ouyang Qi
- 国际基因工程机器大赛对本科生科研教育的启示
- Bringing scientific research education closer to undergraduates through International Genetically Engineered Machine competition
- 生物工程学报, 2018, 34(12): 1923-1930
- Chinese Journal of Biotechnology, 2018, 34(12): 1923-1930
- 10.13345/j.cjb.180452
-
文章历史
- Received: November 2, 2018
- Accepted: December 4, 2018
2 华大基因学院,广东 深圳 518083;
3 北京大学物理学院,北京 100871
2 BGI College, Shenzhen 518083, Guangdong, China;
3 School of Physics, Peking University, Beijing 100871, China
“合成生物学” (Synthetic biology)是在遗传工程(Genetic engineering)的概念提出并实践十多年的大背景下,在DNA测序、DNA合成、计算机建模以及相关定量分析技术进一步成熟的基础上,于21世纪初期兴起的一门交叉学科。进入新千年后,合成生物学领域的研究发展迅速,来自生物、化学、工程、计算机等不同学科的科学家从各自的角度切入生物技术领域,取得了许多精彩的工作成果,其中比较经典的有:加州理工Michael Elowitz等的“生物振荡网络”[1]和波士顿大学James Collins团队的“大肠杆菌拨动开关”[2];德州大学奥斯汀分校和加州大学旧金山分校2004年的iGEM联合参赛项目“生物显示器”[3];加州大学伯克利分校Jay D. Keasling团队的“酵母产青蒿素项目”[4]等。
目前,学界对于“合成生物学”的定义还存在不同认识,其中一个可行的定义是:合成生物学是设计那些自然界中不存在的生物系统以及重新设计天然生物系统的学科;它强调对生物系统有意图的工程设计[5]。所以,合成生物学不同于以前“发现式科学研究”的范式,它主张从“分析”转向“综合”,从“发现”转向“应用”。时至今日,随着基因编辑、DNA测序、生物信息学等技术方法的进一步发展,合成生物学的研究平台也由早期的原核模式生物转向了工业微生物、植物和哺乳动物细胞,其在信息处理、制作材料、化学加工、能源、制药等各个方面的应用前景也得到了学术界和工业界的普遍认可。
国际遗传国际基因工程机械机器大赛[6]——全称international Genetically Engineered Machine Competition (以下简称iGEM)——与合成生物学几乎同时诞生。iGEM最早于2005年由麻省理工学院发起,旨在推动合成生物学学科发展,促进各国大学生在该领域的学习、交流与合作。每年6月,在赛制组委会注册的学生队伍都可以获得一个装有“标准化DNA元件” (Standard parts,以下简称“元件”)的工具箱。随后整个夏季,学生在自己学校运用组委会提供的元件以及自己新开发的元件构建新的生物系统并表达在活细胞中。每年11月初iGEM “欢聚大会” (Jamboree)在麻省理工学院举办,期间各参赛队伍将展示他们的工作,评选出各方面奖项的获得者。大赛总冠军被称为“最终唯一大奖” (The only grand prize),另有针对特定方面的突出表现而专门设计的单项奖。由于其特有的趣味性和应用性,经过十余年的发展,iGEM从最早的麻省理工、加州理工、普林斯顿等五所北美学校的学生暑期联合科研比赛普林斯顿等5所北美学校的学生暑期联合科研比赛,成长为了有上百支队伍(包括本科生、研究生、高中生)参与的大型赛事,成为了最具影响力的世界级大学生学术竞赛之一。
iGEM的成功离不开Drew Endy、Tomas Knight和Randy Rettberg等奠基者和组织者,其中又以Drew Endy对iGEM的影响最为重要。Drew Endy原为麻省理工学院生物工程系助理教授,2008年夏季到斯坦福大学任教,他围绕iGEM的建立和发展做了一系列的工作:1)与Tomas Knight等一同确立了从“元件” (Parts)到“装置” (Device)再到“系统” (System)的合成生物学工程原则[7];2)与Randy Rettberg等一同建立了“标准生物元件注册库” (Registry of standard biological parts)的网站[8];3)主持成立了“生物砖基金会” (Biobricks Foundation,BBF)。“元件-装置-系统”的原则是iGEM把生物系统工程化的理念基础,“标准生物元件注册库”的网站为历届iGEM提供了“元件”信息的存储、交换和检索平台。
作为工程学家,Drew Endy试图把标准化和模块化这两个工程原则引入到基因工程中,希望设计生物系统能够变得如同设计电路一样简单。他认为限制人们对生物系统进行设计的4个关键挑战是:1)生物系统的复杂性;2)构建和描述合成生物系统的繁琐程度及不可靠程度;3)生物系统运行时自发涌现的物理多样性;4)生物系统的突变和进化能力。他继而提出:,对生物系统进行标准化(Standardization)、解偶联化(Decoupling)以及抽象化(Abstraction)的“基础性技术” (Foundational technologies)可能是应对前三个挑战的办法,这样的技术能帮助我们把设计和构建生物系统的工作变得规范化、日常化,从而大大促进合成生物学在各个领域的应用[9]。“标准生物元件注册库”网站、“DNA-元件-装置-系统”的抽象原则以及iGEM竞赛等都是在这个理论背景下对“基础性技术”所作出的探索和尝试。在iGEM竞赛中,每支队伍都需要利用标准化的DNA元件以及自己开发的新元件进行生物系统的设计和构建。这样的主张大幅降低了大学生参与生物系统理性设计和基因工程实验的门槛,直接促进了iGEM比赛的蓬勃发展。
2007年,受大赛组织方的邀请,北京大学、清华大学、天津大学和中国科技大学四所中国地区高校分别组队第一次参加天津大学和中国科技大学4所中国地区高校分别组队第一次参加iGEM比赛。其中,北京大学首次参赛即一举夺得赛会最高奖项“最终唯一大奖” (The only grand prize)。除此之外,四支中国队伍还拿到了两项决赛入围奖4支中国队伍还拿到了两项决赛入围奖、两项单项和四块金质奖章。对于首次参赛的中国队伍来说,这样出色的成绩对iGEM在中国的发展起到了良好的推动作用。伴随着合成生物学学科的飞速发展和iGEM大赛的迅速扩张,越来越多来自中国的学生团队参与其中(图 1)。许多中国团队作出了具有相当原创性和创新性的工作,在赛场上取得了优异成绩。2017年iGEM竞赛达到赛事规模的新顶点,来自世界各地的300余支iGEM队伍齐聚波士顿。其中,来自中国大陆和港台地区的本科、研究生和高中iGEM团队达到了83支,共有79支队伍获得了奖项,其中大陆地区66支,香港特区4支,台湾地区9支。中国大陆地区取得了总计35金,、14银、,17铜的优异成绩,其中大学本科生队伍31金、,11银、,12铜,有12支队伍得到了单项奖或单项奖提名。
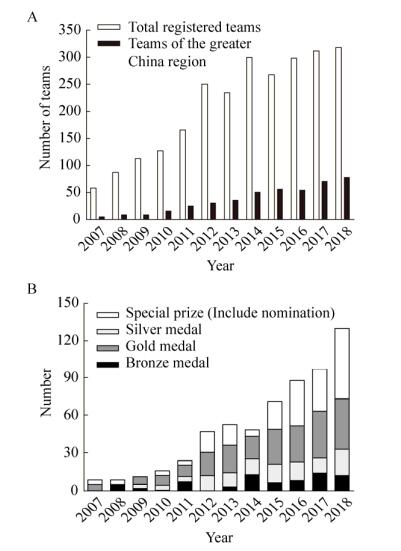
|
| 图 1 中国地区大学队伍参加iGEM大赛情况(A:中国地区iGEM大学团队参赛队伍数目;B:中国地区iGEM大学团队历年获奖数) Figure 1 An overview of Chinese undergraduate teams participate in the iGEM competition. (A) Number of Chinese undergraduate teams participating in the iGEM competition over the years. (B) Number of awards from the iGEM teams in China over the years. |
| |
北京大学自首次参赛以来,在随后的10届iGEM大赛中多次取得优异成绩,包括在2010年获得总决赛亚军(First Runner Up)。相应的参赛项目在比赛以后经过一定时间的深入积累,大部分转化为了发表的学术论文(表 1)。作为国内众多iGEM队伍中的一支,北京大学iGEM的组织模式既继承了iGEM赛事的整体特色,又有着自己独特的优势。
| Year | Awards | Publications |
| 2007 | Gold Medal; Grand Prize | Molecular System Biology, 2010[13] |
| 2009 | Gold Medal | Nature Communications, 2014[14] |
| 2010 | Gold Medal; Best Environment Project; First Runner-Up Prize | Quantitative Biology, 2013[15] |
| 2011 | Gold Medal; Top Sixteen | ACS Synthetic Biology, 2012[16]; PLoS ONE, 2012[17] |
| 2012 | Gold Medal; Best Presentation, Asia; First Runner-Up, Asia | |
| 2013 | Gold Medal; Best Parts Collection, Asia; Best New BioBrick Part, Natural, Asia | ACS Synthetic Biology, 2014[18] |
| 2014 | Gold Medal | Journal of Bioscience and Bioengineering, 2016[19] |
| 2015 | Gold Medal; Best New Composite Part; Best Part Collection | ACS Synthetic Biology, 2016[20] |
| 2016 | Gold Medal; Best Environment Project | ACS Synthetic Biology, 2018[21] |
| 2017 | Gold Medal; Nominated for Best Information Processing Project | Chinese Journal of Biotechnology, preparing2018 |
鉴于iGEM大赛极富学术性、创造性的特点,且参赛同学具有高度自主性,其组织工作与传统学术竞赛有很大区别。iGEM竞赛并非单纯比拼项目的学术价值,还包括评价项目的立意、应用价值、社会影响力的调研分析及展示效果等综合性内容,队伍的队员构成需要高度多样化。北大iGEM团队面向全校招募成员,团队成员可能来自生物、物理、化学、数学、计算机、医学、工程学等各个理工科院系,分布在各个年级。就学术技能而言,有擅长实验操作、学术理论、数学建模、数据分析等不同特长的成员;就队伍运作而言,既需要学术骨干分子和善于项目管理的成员,也需要善于艺术设计和财务管理的成员。成员多样化和多维度团队协作是iGEM赛事的鲜明特点,这在其他本科生竞赛中是稀缺难以见到的。
自2007年首次参赛至今,北大iGEM团队逐渐摸索总结出了一套较为完整成熟的组织运营模式,并在实践中得到了良好验证。北大iGEM通过“北京大学基因机器研究会”这一由学生独立运营的社团开展自主的理论学习、实验训练和备赛活动。在整个活动过程中,由专门的指导委员会给iGEM团队提供学术指导。指导委员会由一到两名教师和若干名往届资深队员组成,教师主要评估团队项目的学术价值和可操作性,并对项目立项和赛前展示等关键环节进行把关。往届资深队员一般是往届队伍中的骨干,他们会从实验经验、项目运作、参赛准备等方面对团队进行跟踪式指导。
北大校方的关心和支持也为iGEM活动提供了坚强后盾。北大iGEM团队在校内的生物实验教学中心拥有两间专有实验室,能满足基本的分子生物学实验和社团活动。由于每年参赛项目不同,学生常需邀请校内相关领域的学者进行指导,甚至借助校内学者实验室进行精密实验,北大宽松自由的学术氛围之下学者们愿意为团队提供关键性的学术帮助。得益于这样的环境和平台,iGEM团队的主观能动性得到最大程度的释放和发挥。
自2016年起,北京大学生命科学学院和前沿交叉学科研究院开办了“合成生物学导论”选修课。课程采用了专题讲座的方式,由本校老师和校外专家就合成生物学的某一个领域或某一个问题作系统性介绍。课程面向全校本科生和研究生开放,既帮助新队员夯实知识基础,也为iGEM团队增添人员储备。课程不设置期末考试,由学生自发组成小组进行头脑风暴和项目设计,并在遴选会上进行报告展示,经提问、讨论等环节,由评委老师进行最终评价并作为成绩评定的重要部分。“合成生物学导论”将iGEM社团的活动和课堂结合起来,同时使iGEM建队、设计选题这一过程的管理更加系统化、和组织化。
基于上述良好的队伍组织模式,北大iGEM团队能够相对高效的地完成备赛和参赛。整个备赛和参赛整个流程可以分为“设计、选题”“设计和选题”、“实验准备和实施”以及“备赛及参赛”三个阶段,我们总结了北大iGEM队伍在各个阶段的经验,以供参考。
2.1 第一阶段:设计选题每届iGEM赛事结束后,往届参赛队员通过海报宣传和宣讲会举办宣讲会等方式在全校范围内进行新成员的招募。招募完成后,便进入比赛准备和设计选题阶段。这一阶段通常从秋季学期的12月开始,进行到下一年春季学期4月。该阶段的主要任务是由iGEM社团组织新一届同学学习合成生物学的基础和前沿知识,提出初步想法并通过头脑风暴选出最终参赛项目。
详细来说,往届参赛队员首先在秋季学期内开展讲座,介绍合成生物学和iGEM比赛的相关概念。秋季学期结束后,往届队员会为新成员组织为期数天的集训营,集中进行相关知识的讲授。在集训营的最后一天,新成员被分成若干学习小组,各小组在随后的寒假内期间自行学习往年优秀iGEM项目并对合成生物学经典文献进行深入调查和阅读,然后定期进行在线交流讨论。这样的方式可以在短时间内让同学们充分认知合成生物学并找到自己的兴趣点。随后,同学们开始进行头脑风暴,在讨论中讲述自己的创意想法(哪怕是非常初级的想法),通过不断的群组讨论进行完善。新成员在春季学期开始前集合,各小组集中汇报寒假的学习成果,并根据“头脑风暴”的结果进行重新分组。
春季学期开始后,团队每周以例会的方式进行项目讨论,同学们用口头报告等形式互讲互评深入交流,进一步完善各自的项目设计。每年4月,由指导委员会组织参赛项目遴选会,对各小组的项目设计进行指导。经过两到三轮的遴选会,从候选项目中确定最终的参赛项目。项目确定后,在4月底,由指导委员会组织一次检验同学们前期参与程度、解决实际问题综合能力的“马拉松式”开卷考试,最终确定本年的正式参赛人员名单。
2.2 第二阶段:实验准备及实施该阶段是从4月底队伍建立起到7月初进入暑假正式开展项目的期间,iGEM团队成员需要在老队员的指导下完成实验技能强化和实验室运营培训。同时,在春季学期的期末考试前,尽可能完善实验的设计,并开展相关的预实验。
暑假开始后,队员们开始正式开展实验工作。在实验最开始阶段,常常会有同学因为没有足够的实验基础导致实验出现问题。遇到队员都没有接触的实验方法,更需要整个团队边学边做,互相帮助,确保每个队员都或多或少参与项目的设计和改进。这为队员们的个人参与度、责任感以及整个团队凝聚力提供了保证。
进入高强度实验阶段后,老队员需要紧密地参与实验设计,帮助解决团队遇到的困难。同时,指导委员会需要定期组织例会,监督实验的进度,保证整个项目有计划地推进。整个暑假,iGEM队员们几乎都需要在实验室中度过,而实验的过程又是相对繁琐、枯燥的,它考验着同学们的意志品质。这一阶段的艰苦工作和团队协作,会进一步激发队伍不畏困难的精神,使整个团队愈发地富有战斗力。
2.3 第三阶段:集中备赛及参赛从9月秋季学期开始,团队将进入集中备赛及参赛阶段。该阶段不仅需要整个团队全力以赴完成剩余的实验任务,还需要进行比赛的准备工作,包括完成建立网站、寄送DNA元件、填写比赛相关材料、制作海报,、准备报告展示等一系列任务。
进入新的学期,课程和学业压力可能会迫使项目的进度放缓。这时,有效的进度评估机制就显得格外重要。北大iGEM指导委员会将会组织定期的进度评估,督促各项任务齐头并进。在多轮细致的指导下,学术海报和展示用幻灯片会经过反复的修改以达到最好效果。在学术汇报展示部分,指导委员会将会安排多轮试讲活动,同时邀请本校的教授作为评委进行点评,以模拟真实的比赛情况。除上台展示的同学外,其他队员们需要针对项目,详细周全地准备评委可能会问到的问题,完善展示的细节,以做好最充分的准备。
由学生自主完成项目和实验设计,将严肃而活泼的学术讨论氛围贯穿始终,这是北大iGEM队伍一贯坚持的传统。这样的组织模式为本科生搭建了一个具有较大自主性的、可得到全方位锻炼的科研平台。该平台包括科研入门培训、研究性学习方式、资金支持、实验环境支持、导师和课程指导等学术环境,以及参与国际比赛、学术会议或发表论文等多元化的科研产出途径,从而实现了本科生科研活动的可持续性自我成长。
3 北京大学iGEM活动意义的分析北大iGEM活动是一个完全由学生自主发起、组织的科研活动,其模式的成功对如何培养研究型大学本科生科研能力有很大的借鉴意义。参照iGEM在中国以及全世界的发展状况,以及北大iGEM团队十年来的发展经验,我们不难分析出以下事实:一种以学生为主的、尊重学生的科研地位、提供学生学术资源的教育模式逐渐兴起,并在学生群体中的需求仍呈逐年扩大化扩大的趋势。
3.1 iGEM活动代表了以学生为主体的科学研究培养模式iGEM的诞生地麻省理工学院于1969年推出了美国第一个本科生科研能力培养项目“本科生研究机会项目” (Undergraduate research opportunities program,简称UROP[10]),这一项目鼓励本科生以年轻同事的身份参与到教师的科研工作中,要求学生独立撰写研究计划及项目总结,并且学校通过给予学分、报酬或者“志愿者”身份来保障学生在研究过程中的积极性。麻省理工的另一个培养项目是历史悠久的“独立活动时期计划” (Independent activities period,简称IAP),即在圣诞节后的四周时间里,鼓励老师和同学们打破平常的身份限制,提出项目、共同合作。这时既可以像往常一样由老师提出项目学生参与,也可以反过来由学生提出项目老师参与。可见,麻省理工学院非常注重学生的主体性,并且有一套完整的保障机制,激励本科生参与到科研活动中。继麻省理工学院之后,美国其他学校也都开展了不同形式的鼓励本科生参与科研活动的项目,并取得了很多进展[11-12]。iGEM正是在美国研究型大学开展本科生科研训练40多年的大背景下诞生的,它所提出的“参赛流程”反映了美国研究型大学组织本科生科研能力培养的先进理念和发达制度。
不仅如此,iGEM主办方推荐的“标准参赛流程”还用工程化的方法简化了生物工程研究项目的复杂度:其标准生物元件(Standardized bioBricks)的概念、相应的标准化DNA拼接技术(Standard assembly)以及在此基础上的一系列系统工程原则,都从技术上进一步降低了参与者的进入门槛,从而更加有利于本科生开展原创的生物工程项目实践。在这一过程中,学生自主性的学习和讨论是科研教育的主体,而教师通常只起到方向指导和教学评估的作用。
3.2 iGEM活动弥补了我国高校当前“学徒式”培养模式的不足在国内的高等院校和研究型大学里,教师同时担有研究和授课的任务,研究多面向研究生、,授课多面向本科生。为了让学生较早适应研究生阶段的工作,教师往往会接收高年级本科生进入实验室参与教师的科研项目。各大高校也设置了各类本科生科研训练制度和“基金”项目,以期激励本科生深度参与到科研活动中。然而,大部分学子在大一和大二阶段有较重的课业压力,在开展研究课题时其实对实验室工作及相关知识概念的了解有限;教师也担心学生因缺乏经验导致项目不能完成,浪费资源。鉴于以上两点,“课题立项”在实际操作中多由老师代办,从而使其成为教师项目的一部分。由于学分和结题的压力,本科生科研训练常常变为教师主导,、学生干活的“学徒式”的培养模式。
学徒并非不好,以教师为主也并非不好,但如果一味由教师安排学习内容,教师为学生制定教学计划、科研计划,学生始终处在被动的状态,不利于调动学生的主动性,、激发学生的创造力,也不利于培养学生自主追踪和拓展前沿研究方向的能力。而在科研人才培养的第一个阶段,也是学术生涯中能力建设的关键期“——本科生阶段”——有意识地培养科研的主体性,能从根本上促进这些未来科研工作者的自主创新能力。
3.3 iGEM活动给年轻学子提供主导独立科研项目的机会在国内高校现有教育环境下,iGEM活动为本科生提供了难能可贵的科研教育实践经验。iGEM大赛的评价机制尤其看重参赛学生的自主程度和独立科研能力。在此机制下,iGEM学生自发性的地进行队伍组建、社团活动、项目调研、经费申请、实验室管理、社会调研、行政管理等工作。这充分发挥了学生的主体性,使得学生的个人能力得到了最大程度的培养。
一般来说,同学们在iGEM比赛所横跨的10个月内将会获得以下收获:1)主导一项独立的科研项目,通过项目制学习接受全方位的科研训练;2)健全团队合作的意识,获得团队管理和组织协调的经验;3)完成一项学术水平较高的科研工作,并在赛场上获得国际学术同行的评价;4)如果在比赛中收获优异成绩,将会为在未来学术生涯中获得一个高起点;5)赛后可继续深入研究,将参赛项目成果在学术期刊发表。上述这些都是传统意义上的科研教育模式难以提供的。
4 总结与展望十年的北大iGEM活动为本科生团队创造了良好的学术价值和社会成就,也让我们看到本科生课外科研所能达到的高度,其模式是值得肯定和推广的。我们可以简要归纳出北大iGEM活动的成功要素,为本科生科研教育提供一些经验和启示。
首先,一个富有吸引力的学术契机是活动成功的关键所在。iGEM大赛是本科生团队合作完成科研项目的天然契机:它既有可见的短期的收益——即在国际大赛中获得奖项,又有长期的学术价值——在本科阶段即完成初步的科研训练、甚至发表科学论文,对未来的升学与求职会有很大帮助。iGEM大赛综合了自主性、创新性、趣味性,能充分调动年轻学子的创造力和主观能动性。
其次,高水平的教师指导是科研教育产生显著效果的必要条件。iGEM大赛虽然强调以学生为主体、自主立项、自主科研,但全无学术背景的学生很难独立提出既有学术价值又有可操作性的科研项目。因此,需要有经验丰富的教师和有经验的研究生、高年级本科生给予及时的指导,避免出现盲目和无效的项目实践。经验丰富的指导者团队能很好的地把控立项和设计的节奏,引导同学们高效行事,快速掌握科学的思维和方法。
最后,应当建立完整的项目评价机制。本科生更多时候需要引导、激励和肯定,建立一套完整的评价体系可以保护学生的积极性,使他们学会直面挫折,并享受成功的快乐。来自学校和社会的关注也能增强学生们的项目积极性。
综上,iGEM模式在北大以及各大高校的成功经验,对高校以学生为主体的研究型本科生科研能力培养能养有着重要的借鉴意义。随着iGEM模式的科研教育在国内的蓬勃发展,我们期待未来在这种模式下培养的年轻学子能够具备更为扎实的能力结构与更为全面的知识图景,成为即将到来的新一轮技术革命的中流砥柱。
| [1] | Elowitz MB, Leibler S. A synthetic oscillatory network of transcriptional regulators. Nature, 2000, 403(6767): 335–338. DOI: 10.1038/35002125 |
| [2] | Gardner TS, Cantor CR, Collins JJ. Construction of a genetic toggle switch in Escherichia coli. Nature, 2000, 403(6767): 339–342. DOI: 10.1038/35002131 |
| [3] | Levskaya A, Chevalier AA, Tabor JJ, et al. Synthetic biology: engineering Escherichia coli to see light. Nature, 2005, 438(7067): 441–442. DOI: 10.1038/nature04405 |
| [4] | Ro DK, Paradise EM, Ouellet M, et al. Production of the antimalarial drug precursor artemisinic acid in engineered yeast. Nature, 2006, 440(7086): 940–943. DOI: 10.1038/nature04640 |
| [5] | Weiss R. Synthetic biology: from modules to systems//Proceedings of the 20th symposium on Great lakes symposium on VLSI. Providence, Rhode Island, USA: ACM, 2010: 171-172. |
| [6] | Smolke CD. Building outside of the box: iGEM and the BioBricks Foundation. Nat Biotechnol, 2009, 27(12): 1099–1102. DOI: 10.1038/nbt1209-1099 |
| [7] | Canton B, Labno A, Endy D. Refinement and standardization of synthetic biological parts and devices. Nat Biotechnol, 2008, 26(7): 787–793. DOI: 10.1038/nbt1413 |
| [8] | Registry of Standard Biological Parts[EB/OL].[2018-06-01]. http://parts.igem.org/Main_Page. |
| [9] | Endy D. Foundations for engineering biology. Nature, 2005, 438(7067): 449–453. DOI: 10.1038/nature04342 |
| [10] | Wong NYJ. An Exploratory Research Study of Massachusetts Institute of Technology's Undergraduate Research Opportunities Program (UROP): The Impact of Student-Supervisor Relationships. Online Submission, 2014, ERIC Document Reproduction Service No. ED491017. |
| [11] | Russell SH, Hancock MP, McCullough J. Benefits of undergraduate research experiences. Science, 2007, 316(5824): 548–549. DOI: 10.1126/science.1140384 |
| [12] | Hunter AB, Laursen SL, Seymour E. Becoming a scientist: the role of undergraduate research in students' cognitive, personal, and professional development. Sci Educ, 2007, 91(1): 36–74. DOI: 10.1002/(ISSN)1098-237X |
| [13] | Lou C, Liu X, Ni M, et al. Synthesizing a novel genetic sequential logic circuit: a push-on push-off switch. Mol Systems Biology, 2010, 6(1): 350. |
| [14] | Zhang H, Lin M, Shi H, et al. Programming a Pavlovian-like conditioning circuit in Escherichia coli. Nat Communic, 2014, 5: 3102. DOI: 10.1038/ncomms4102 |
| [15] | Zhang H, Sheng Y, Wu Q, et al. Rational design of a biosensor circuit with semi-log dose-response function in Escherichia coli. Quant Biol, 2013, 1(3): 209–220. DOI: 10.1007/s40484-013-0020-4 |
| [16] | Chen S, Zhang H, Shi H, et al. Automated design of genetic toggle switches with predetermined bistability. ACS Synthetic Biology, 2012, 1(7): 284–290. DOI: 10.1021/sb300027y |
| [17] | Ji W, Shi H, Zhang H, et al. A formalized design process for bacterial consortia that perform logic computing. PLoS ONE, 2013, 8(2): e57482. DOI: 10.1371/journal.pone.0057482 |
| [18] | Xue H, Shi H, Yu Z, et al. Design, construction, and characterization of a set of biosensors for aromatic compounds. ACS Synthet Biol, 2014, 3(12): 1011–1016. DOI: 10.1021/sb500023f |
| [19] | Zhang Z, Meng L, Ni C, et al. Engineering Escherichia coli to bind to cyanobacteria. J Biosci Bioeng, 2017, 123(3): 347–352. DOI: 10.1016/j.jbiosc.2016.09.010 |
| [20] | Zhang Y, Qian L, Wei W, et al. Paired design of dCas9 as a systematic platform for the detection of featured nucleic acid sequences in pathogenic strains. ACS Syntheti Biol, 2016, 6(2): 211–216. |
| [21] | Yang X, Wei J, Wang Y, et al. A genetically encoded protein polymer for uranyl binding and extraction based on the SpyTag-SpyCatcher chemistry. ACS Synthet Biol, 2018, 7(10): 2331–2339. DOI: 10.1021/acssynbio.8b00223 |
 2018, Vol. 34
2018, Vol. 34




